糖果派对-糖果派对试玩
分子酶学工程教育部重点实验室韩葳葳教授、韩璐教授研究团队在基于AI的蛋白-配体相互作用研究方面取得重要进展。该研究围绕药物-靶标结合位点和结合亲和力预测的核心难题,构建了多模态蛋白-配体交叉注意力框架,系统整合蛋白序列表示、三维结构特征与配体分子图信息,并引入实验条件信息以提升模型的稳定性与泛化能力。研究进一步实现了结合亲和力预测与蛋白结合口袋识别的统一建模,为虚拟筛选与理性药物设计提供了新的技术路径和理论支撑。研究成果于2026年2月12日在国际学术期刊《Journal of Medicinal Chemistry》上发表。

药物-靶标结合亲和力(DTA)的准确预测仍然是药物发现领域的核心挑战之一,其难点在于需要整合蛋白和配体在序列、三维结构以及理化性质等方面的异构信息。为此,我们提出了 PLMCA多模态蛋白-配体交叉注意力框架,在统一架构中融合两种蛋白语言模型的序列嵌入表示、三维几何特征、理化描述符以及配体分子图表示。PLMCA 进一步将 ChEMBL 数据库中的实验测定条件作为辅助输入,以减轻批次效应并降低测量噪声。 在 PDBbind21 数据集上,PLMCA 在随机划分、未见配体和未见蛋白等多种评估设置下,对 Kd 和 Ki 的预测性能达到或优于当前先进方法。在 ChEMBL_mini 数据集上,PLMCA 在 IC50、Kd 和 Ki 预测任务上分别取得 0.531、0.635 和 0.519 的 R² 值。此外,PLMCA 在蛋白结合口袋预测方面同样表现稳健,在未见蛋白设置下的 AUPR 最高可达 0.655。同时,团队开发并上线了 PLMCA 在线预测平台(//hwwlab.com/webserver/plmca),支持结合药物-靶标的位点识别与亲和力预测,为科研人员提供便捷高效的智能分析工具。
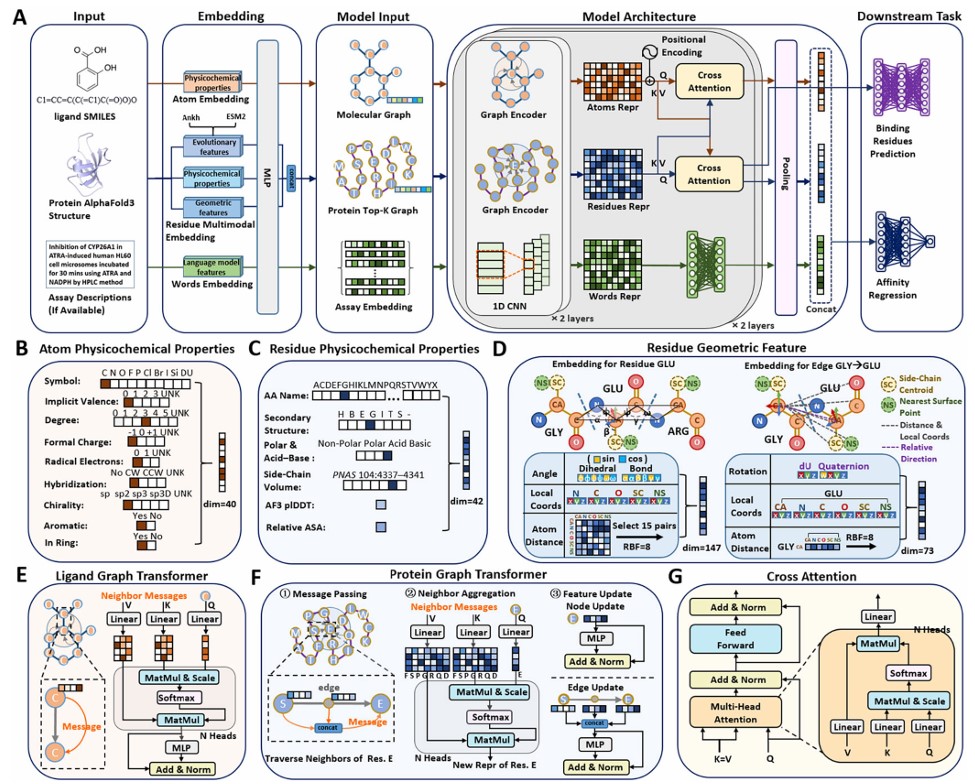
图1. 多模态蛋白配体相互作用模型PLMCA架构图
该论文第一完成单位为糖果派对-糖果派对试玩
;吉林大学博士研究生贺奕为论文第一作者,韩葳葳教授和韩璐教授为共同通讯作者。本研究得到了国家自然科学基金面上项目(32471313)的资助。
全文链接//pubs.acs.org/doi/10.1021/acs.jmedchem.5c03431